Population-level transcriptome study of reproductive traits of the Pacific and Portuguese oysters
Basée sur l'existence d’une différenciation génétique et phénotypique entre populations d’huître creuse du Pacifique Crassostrea gigas et d’huître creuse portugaise Crassostrea angulata, la présente étude vise à comparer les caractères de reproduction de C. gigas, C. angulata et de leurs hybrides. Pour ce faire, nous avons mis en place une expérience de jardin commun basée sur la comparaison de descendances d'huîtres sauvages du Pacifique originaires de France et d'huîtres creuses portugaises originaires du Portugal et de leurs deux descendances hybrides (C. gigas femelles croisées avec C. angulata mâles GA et inversement AG). Le sex-ratio, le stade de gamétogenèse, l'effort de reproduction, l'indice de condition ont été analysés chez 100 huîtres par descendance. L'expression génique à haut débit basée sur la méthodologie RNAseq a été analysée dans neuf gonades matures femelles par descendance. Un effet maternel sur le transcriptome des gonades femelles matures a été observé, reflétant des signaux moléculaires gonadiques propres au taxon. Plusieurs transcrits sont apparus différemment exprimés entre les descendances de C. gigas et C. angulata. Les transcrits candidats coderaient pour des protéines majeures impliquées dans le contrôle et le succès de la reproduction supposément impliqué dans les différences observées dans les traits de gamétogenèse. Une meilleure qualité des gamètes peut être déduite de C. gigas considéré comme un avantage adaptatif pour coloniser les habitats en lien avec son caractère invasif.
Simple
- Title
-
Population-level transcriptome study of reproductive traits of the Pacific and Portuguese oysters
- Date (Creation)
- 2013-03-01
- Date (Publication)
- 2019-10-15
- Citation identifier
- FR-330-715-368-00032-DATARMOR-BIOINFO_GIGALATA
- Citation identifier
- DOI:10.12770/df5b36e7-ea13-462a-ae45-6a4ddef283bf
- Abstract
-
Basée sur l'existence d’une différenciation génétique et phénotypique entre populations d’huître creuse du Pacifique Crassostrea gigas et d’huître creuse portugaise Crassostrea angulata, la présente étude vise à comparer les caractères de reproduction de C. gigas, C. angulata et de leurs hybrides. Pour ce faire, nous avons mis en place une expérience de jardin commun basée sur la comparaison de descendances d'huîtres sauvages du Pacifique originaires de France et d'huîtres creuses portugaises originaires du Portugal et de leurs deux descendances hybrides (C. gigas femelles croisées avec C. angulata mâles GA et inversement AG). Le sex-ratio, le stade de gamétogenèse, l'effort de reproduction, l'indice de condition ont été analysés chez 100 huîtres par descendance. L'expression génique à haut débit basée sur la méthodologie RNAseq a été analysée dans neuf gonades matures femelles par descendance. Un effet maternel sur le transcriptome des gonades femelles matures a été observé, reflétant des signaux moléculaires gonadiques propres au taxon. Plusieurs transcrits sont apparus différemment exprimés entre les descendances de C. gigas et C. angulata. Les transcrits candidats coderaient pour des protéines majeures impliquées dans le contrôle et le succès de la reproduction supposément impliqué dans les différences observées dans les traits de gamétogenèse. Une meilleure qualité des gamètes peut être déduite de C. gigas considéré comme un avantage adaptatif pour coloniser les habitats en lien avec son caractère invasif.
- Credit
-
Projet Aquagenet
- Point of contact
-
Organisation name Individual name Electronic mail address Role IFREMER
Lapegue Sylvie
Author IFREMER
Huvet Arnaud
Author IFREMER
Quillien Virgile
Author IFREMER
Degremont Lionel
Author Instituto Nacional de Recursos Biológicos
Batista Frederico
Author IFREMER
Boudry Pierre
Author IFREMER
Begout Marie-Laure
Author IFREMER
Publisher
-
GEMET - INSPIRE themes, version 1.0
-
-
Habitats and biotopes
-
-
Thèmes Sextant
-
-
/Biological Environment/Habitats
-
-
ODATIS aggregation parameters and Essential Variable names
-
-
Bioinformatics
-
- Use limitation
- CC-BY (Creative Commons - Attribution)
- Access constraints
- License
- Use constraints
- License
- Spatial representation type
- Grid
- Language
- Français
- Character set
- UTF8
- Topic category
-
- Oceans
))
- Reference system identifier
- EPSG / WGS 84 (EPSG:4326) / 8.6
- Topology level
- Geometry only
- Number of dimensions
- 2
- Dimension name
- Column
- Dimension name
- Row
- Cell geometry
- Area
- Distribution format
-
Name Version
- OnLine resource
-
Protocol Linkage Name NETWORK:LINK
/home/ref-bioinfo-public/ifremer/pfom/gigalata WWW:DOWNLOAD-1.0-link--download
https://data-dataref.ifremer.fr/bioinfo/ifremer/pfom/gigalata/ Download link
WWW:LINK-1.0-http--metadata-URL
http://dx.doi.org/10.12770/df5b36e7-ea13-462a-ae45-6a4ddef283bf DOI du jeu de donnée
- Hierarchy level
- Dataset
- Statement
-
L'échantillonnage a été réalisé sur les gonades d'huîtres en juin 2012. Les analyses histologiques ont été faites et ont permis le tri des individus sur leurs caractéristiques de reproduction. L’ARN total de 36 individus (9 par descendance) a été utilisé pour constituer 36 librairies, séquencés sur 6 lignes de séquenceur Illumina Hiseq2000 (séquences de type paired-end, 2x100 pb).
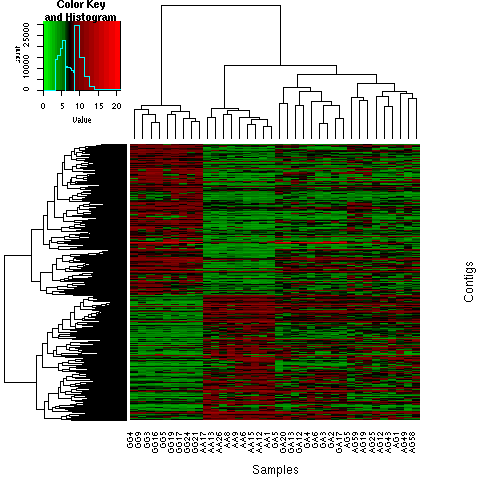
Légende de la vignette :
Cartographie d'activité des gènes différentiellement exprimés entre les descendances, Crassostrea gigas, C. angulata et leurs deux hybrides. Des clusters de 5 903 gènes (rangées) différentiellement exprimés ont été obtenus en utilisant la corrélation de Pearson. Les gènes montrant un profil d'expression similaire sur tous les échantillons sont regroupés (colonnes). AA: descendance Crassostrea angulata; GG: descendance Crassostrea gigas; GA: descendance hybride obtenue en croisant des femelles de C. gigas avec des mâles de C. angulata; AG: descendance hybride obtenue en croisant des femelles de C. angulata avec des mâles de C. gigas. La couleur représente l'expression normalisée (DESeq2), les niveaux d'expression étant représentés avec une échelle de couleurs, dans laquelle les nuances de rouge représentent une expression plus élevée et les nuances de vert représentent une expression inférieure.
Metadata
- File identifier
- df5b36e7-ea13-462a-ae45-6a4ddef283bf
- Metadata language
- Français
- Other language
-
Language Character encoding English UTF8
- Character set
- UTF8
- Hierarchy level
- Dataset
- Date stamp
- 2021-08-12T15:49:38
- Metadata standard name
-
ISO 19115:2003/19139 - SEXTANT
- Metadata standard version
-
1.0
- Metadata author
-
Organisation name Individual name Electronic mail address Role IFREMER
Huvet Arnaud
Local service desk
accessData
Overviews